HiPub: Nuovo strumento di ricerca per connettere geni, proteine, farmaci e malattie.
Posted by giorgiobertin su agosto 4, 2016
Ogni giorno, più di 3.000 nuovi abstracts sono caricati su PubMed, la principale banca dati di riferimento della letteratura biomedica. Qualsisi ricercatore ha grosse difficoltà a rimanere aggiornato sul suo campo di ricerca. Ora un nuovo strumento di ricerca messo a punto dall’AC Tan lab presso l’University of Colorado Cancer Centera e descritto sulla rivista “Bioinformatics” aiuterà i ricercatori a connettere le diverse aree di ricerca inserendo delle semplici parole.
HiPub è uno strumento gratuito, scaricabile per il download come plugin per il browser Chrome.
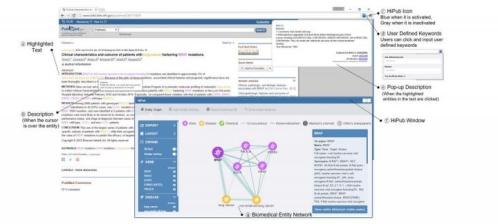
“HiPub analizza tutto il testo e cerca di riconoscere tutto ciò che viene denominato gene, proteine, farmaco e malattie. Estrae tutte le informazioni e le visualizza in una rete. Soprattutto nel campo della biologia molecolare o biologia del cancro, è utile vedere tutte le connessioni nel loro contesto biologico“, dice Aik Choon Tan uno degli autori della ricerca.
Esempio: Un ipotetico ricercatore sta leggendo un articolo che tratta dei geni KRAS e MEK, noti per influenzare lo sviluppo di alcuni tumori. Vuole sapere se questi geni hanno qualche rilevanza per la sua specialità, sono correlati a p53 [un altro gene noto per influenzare il cancro].
La query da inserire è “P53”, mentre sta leggendo l’articolo. HiPub visualizza immediatamente le connessioni tra geni, proteine, farmaci e malattie.
HiPub è un modo per utilizzare text mining per semplificare il processo di scoperta della conoscenza.
Leggi abstract dell’articolo:
HiPub: Translating PubMed and PMC Texts to Networks for Knowledge Discovery
Kyubum Lee, Wonho Shin, Byunggun Kim, Sunwon Lee, Yonghwa Choi, Sunkyu Kim, Minji Jeon, Aik Choon Tan, and Jaewoo Kang
Bioinformatics (2016) doi: 10.1093/bioinformatics/btw511 First published online: August 2, 2016
HiPub and detailed user guide are available athttp://hipub.korea.ac.kr.







Lascia un commento